2026年2月6日,广西大学农学院、广西甘蔗生物育种实验室、亚热带农业生物资源保护与利用国家重点实验室张积森团队牵头,联合福建农林大学、云南农科院等单位在Science上发表了题为“Multiscale pangenome graphs empower the genomic dissection of mixed-ploidy sugarcane species”的研究论文(Research Article)。该研究首次构建了覆盖现代甘蔗主栽品种及其野生祖先物种的多尺度图形泛基因组(super-pangenome graph),在此基础上系统解析甘蔗复杂混合倍体基因组结构,提出适用于高倍体作物的剂量感知关联分析(DosageGWAS)新方法,成功锁定一批与分蘖数、产量、含糖量和叶片角度等重要农艺性状相关的关键基因,并通过CRISPR基因编辑验证了SaTB1基因显著促进分蘖、成倍提高甘蔗产量的功能。这一工作不仅为甘蔗高产优质育种提供了全新的“基因资源地图”和分析工具,也为小麦、棉花、马铃薯等复杂多倍体作物的基因发掘与分子设计育种提供了可直接借鉴的技术路线。
这一成果是张积森团队围绕甘蔗生物育种主线,以甘蔗基因组—种质资源演化—多倍体遗传—重大育种价值基因挖掘为研究链条,继2018年(Zhang et al., Nature Genetics)、2022年(Zhang et al., Nature Genetics)、2023年(Wang et al., Nature Plants)、2025年(Zhang et al., Nature Genetics)等一系列系统性代表性成果之后,在该领域取得的又一重大进展。

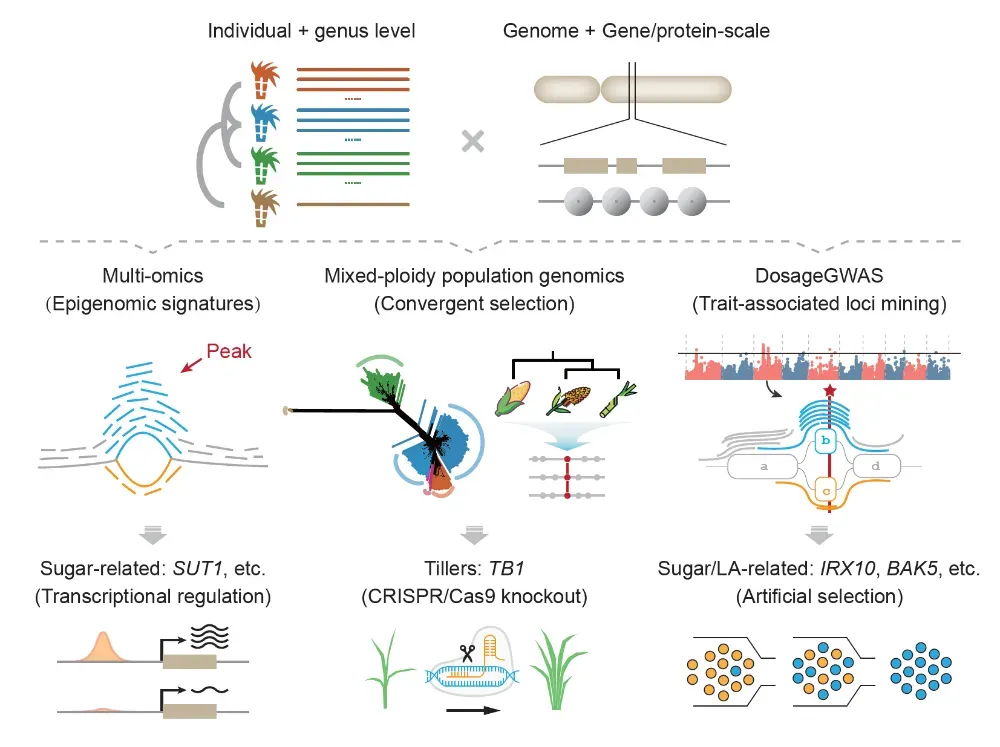
图1.甘蔗复杂多倍体图泛基因组策略提升育种关键基因挖掘
一、支撑全球“糖罐”和“油罐”的作物,为何基因组如此难解?
甘蔗(Saccharum spp.)是全球最重要的糖料和能源作物之一,提供了世界约 80% 的食糖和 40% 的燃料乙醇。现代栽培甘蔗品种源于高含糖的热带种甘蔗(S. officinarum)与高抗逆的野生甘蔗(S. spontaneum)在一个多世纪前的杂交回交,其基因组呈现出极端复杂的结构特征:倍性高达 8–10 倍甚至更高,染色体数目在 100–130 条之间;同源多倍体与异源多倍体成分并存;染色体断裂、融合和非整倍体现象普遍;重复序列和转座子高度富集。这些特征使得传统的单一线性参考基因组难以同时容纳不同倍性、不同染色体数和不同遗传背景,等位基因剂量难以准确区分,测序数据在比对过程中出现大量多重比对和信息丢失等问题。研究指出,传统“单一线性基因组”范式在甘蔗等复杂多倍体作物中已接近失效,亟需新的基因组参考体系。
二、技术突破:从9套基因组到一张“多尺度甘蔗超级图谱”
针对上述挑战,研究团队构建了多尺度图谱泛基因组框架。研究选取了覆盖甘蔗属及近缘种的 9 套染色体水平基因组,包括野生近缘种蔗茅(Erianthus rufipilus)、不同类型的割手密种(S. spontaneum)、热带种甘蔗(S. officinarum)代表材料以及3个现代主栽甘蔗品种。研究者通过无参考的染色体“社区”构建方法,将来自不同物种和倍性的染色体按序列相似性划分为 10个“染色体群落”,对应甘蔗祖先的 10 条原始染色体,建立了跨物种、跨倍性的统一坐标体系。在此基础上,研究利用图结构将 47–57 条单倍型路径压缩到同一坐标框架中,形成包含约 425.9 万个节点、累计长度约 14.7 Gb 的超级泛基因组图谱。在总体序列长度约 43.2 Gb 的情况下,该图谱实现了约 34% 的压缩率,同时捕获了约 82% 的甘蔗基因组多样性,而现有最优单一参考基因组仅能覆盖约34%。这意味着绝大多数自然变异首次被纳入一个统一、可解析的框架中。
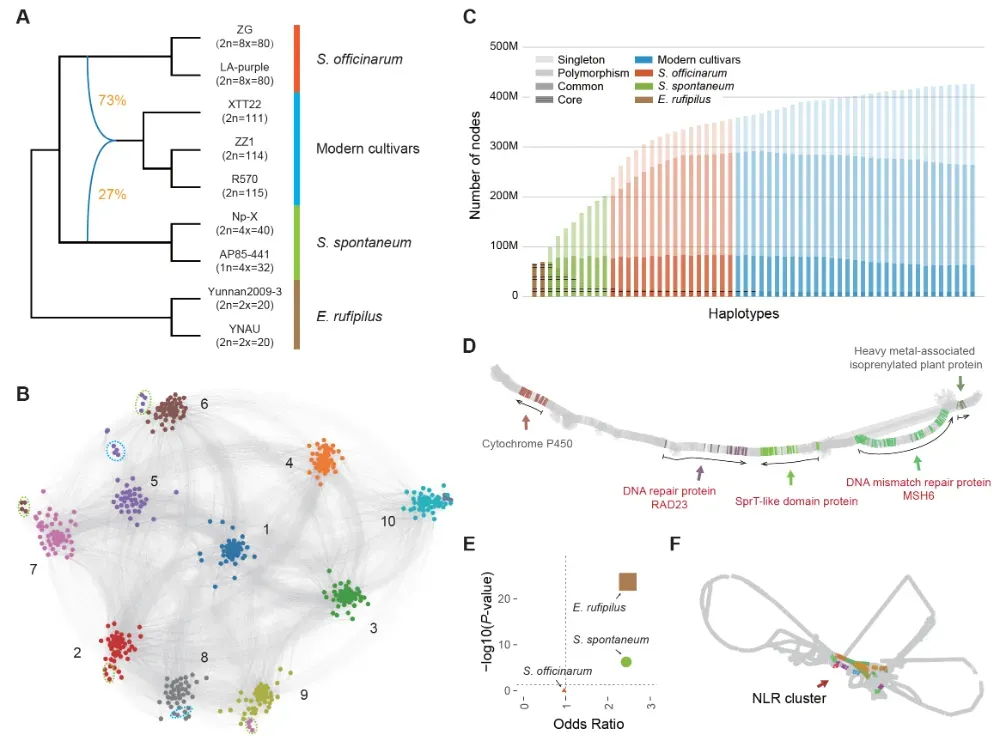
图2.甘蔗属相关染色体群落与图泛基因组
三、图谱加持的多组学:“看清”多倍体基因调控
在建立统一的图谱参考体系后,研究团队以此为基础构建了开放染色质图谱、转录组图谱和甲基化图谱,并与传统线性参考进行了系统比较。结果显示,在代表性材料 S. officinarum(LA-purple)和 S. spontaneum(SES-208)中,图谱参考在保持总体比对率相当的同时,“唯一比对读段”比例显著提升,较单倍体线性参考提高2倍以上,较等位基因级线性参考提高10倍以上,大幅增强了有效信号获取能力。基于图谱分析,研究还识别出 6800–19000 余个仅在线性参考中无法检测的新增开放染色质区域,这些区域富集大量等位变异,揭示了不同物种间转录因子结合位点的系统性差异。以关键蔗糖转运基因 SUT1 为例,图谱显示家种甘蔗特有的上游开放染色质区域与其更高的基因表达水平和更强的糖分运输能力高度一致,为等位特异性调控提供了直接证据。在 RNA-seq 和全基因组甲基化测序分析中,图谱同样显著提高了读段比对质量和甲基化位点检出率。这表明,在高倍体基因组中,图谱泛基因组是连接“序列多样性”和“功能调控差异”的更可靠桥梁。
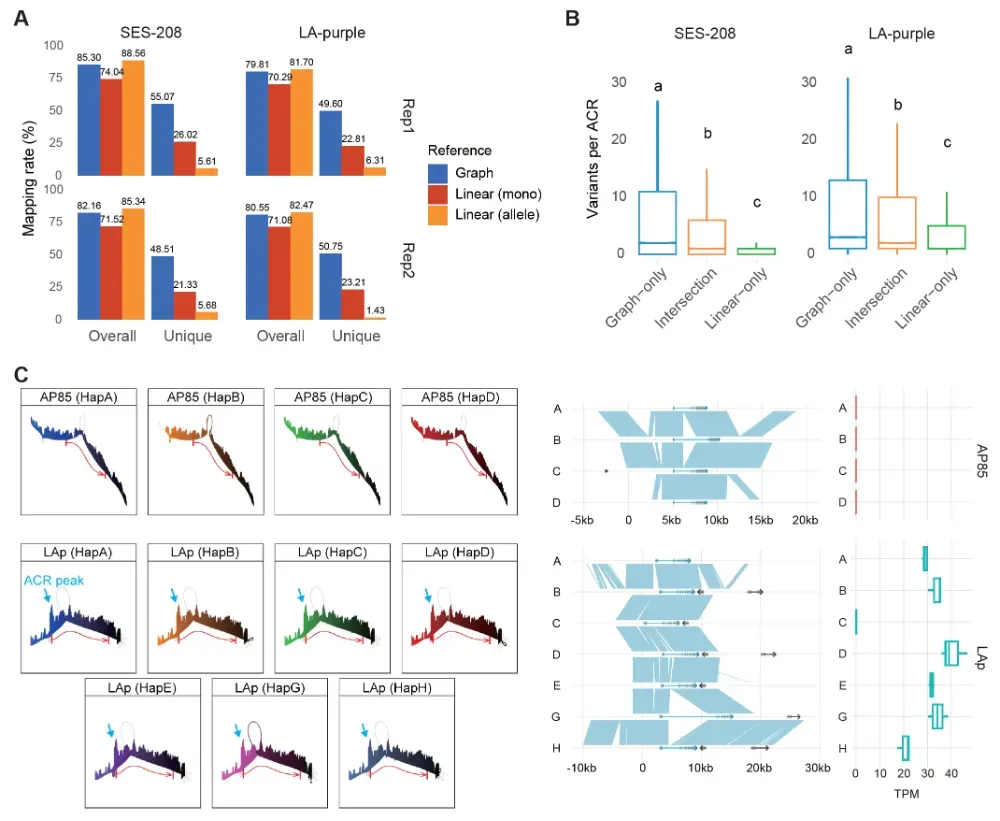
图3. 基于甘蔗属图泛基因组的ATAC-seq分析
四、417份材料的大规模群体遗传:驯化足迹与趋同选择“一网打尽”
依托超级泛基因组,研究团队对 417 份甘蔗及其近缘材料开展了系统的图谱比对和群体遗传分析,材料涵盖野生甘蔗、家种甘蔗、现代栽培品种及近缘种等多个类群。研究共获得 774 万余个高质量 SNP,并对等位剂量进行精确估算。群体结构和系统发育分析结果清晰区分了不同物种与杂交群体,证实现代栽培甘蔗中约 70–90% 的遗传成分来源于热带种甘蔗(S. officinarum),并系统量化了不同类群之间的遗传分化与基因组渗入特征。在此基础上,研究进一步开展跨种群选择扫描,重点比较高糖的热带种(S. officinarum)与高抗逆的割手密种(S. spontaneum),在全基因组范围内识别出约 43 Mb 的选择清扫区域。这些区域显著富集于碳水化合物和淀粉/蔗糖代谢、植株结构发育及抗逆响应等功能通路,锁定了一批与糖运输和代谢、株型与分蘖、开花期及逆境适应相关的关键候选基因,其中超过一半仅在图谱分析框架下得以发现。在更大的进化尺度上,研究将甘蔗与同属黍亚科的高粱和玉米进行比较,发现甘蔗与高粱之间存在显著富集的共选基因对,主要涉及碳代谢和激素及胁迫响应通路,而与玉米的共选基因对数量明显较少。上述结果从群体基因组学层面揭示了“高糖、高生物量型”作物在驯化和改良过程中,围绕碳代谢和应激响应模块经历了高度趋同的人工选择。
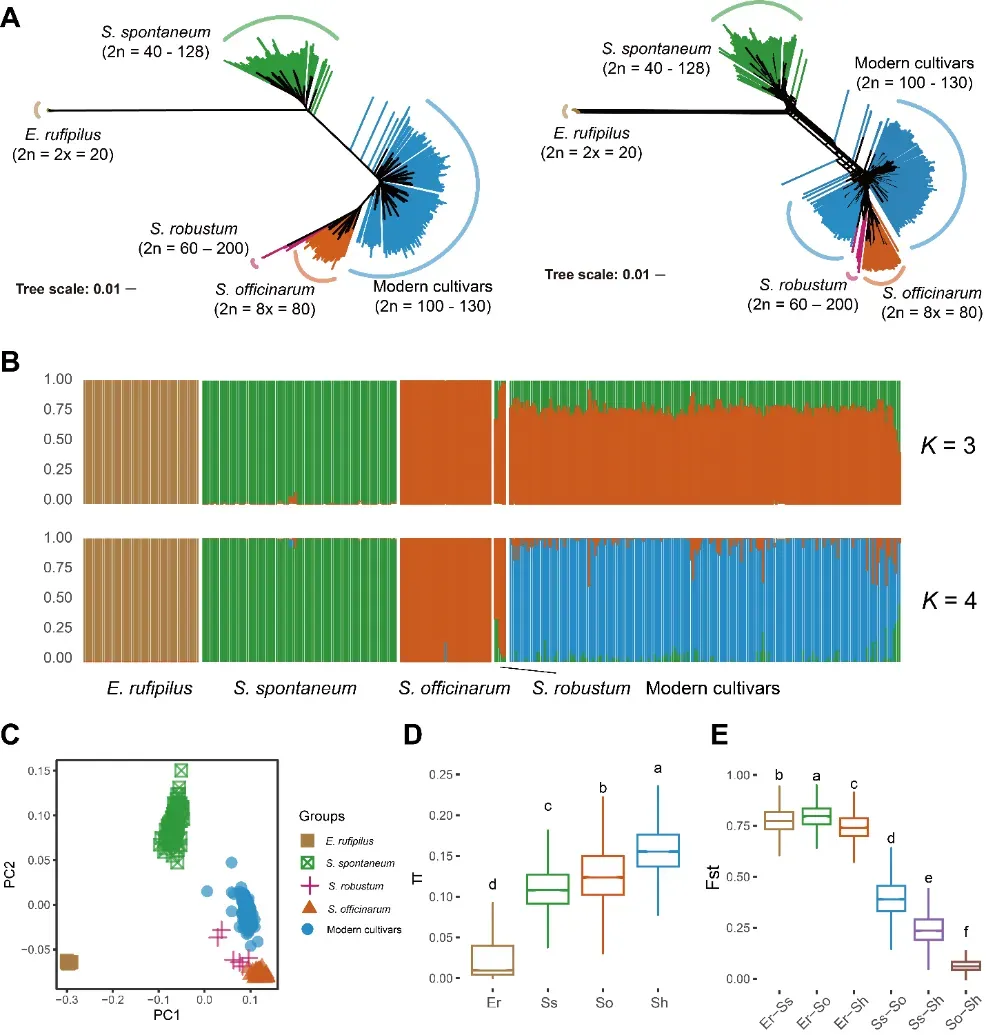
图4. 甘蔗属群体结构和遗传多样性
五、功能验证:编辑一个经典“驯化基因”,甘蔗分蘖翻数倍,产量有望得到大幅度提升
在众多候选基因中,研究团队重点解析了黍亚科中经典的驯化基因 TB1(TEOSINTE BRANCHED1)。该基因曾驱动玉米由多分枝的野生类型演化为少分枝、高产的现代栽培型,被认为是作物驯化的重要里程碑基因之一。研究发现,在蔗茅(E. rufipilus)、高粱和玉米之间,TB1 所在基因组区域具有高度共线性;在已驯化或栽培的类群中,TB1 周围的遗传多样性显著下降,表明其在演化过程中受到强烈人工选择。相比之下,八倍体热带种甘蔗(S. officinarum)中 TB1 区域的多样性下降幅度较小,提示在高倍体背景下,驯化过程中等位基因更难被完全固定,这也与甘蔗仍保持一定分蘖能力的田间表现相一致。为验证 TB1 在甘蔗中的功能,研究团队利用 CRISPR/Cas9 技术对热带种(S. officinarum)中的 SaTB1 进行定向敲除,获得 21 条不同编辑效率的突变系,其中部分材料的等位协同编辑效率超过80%。与野生型相比,高效突变材料的分蘖数提高约4.0–4.6 倍,分蘖启动显著提前,单位面积蔗茎产量提升约 3.8–4.5 倍,且相关性状与编辑效率呈显著正相关。研究表明,SaTB1 是控制甘蔗分蘖和产量的关键驯化基因,传统驯化未能完全“用尽”其潜力,通过定向基因编辑有望实现产量的跨越式提升。
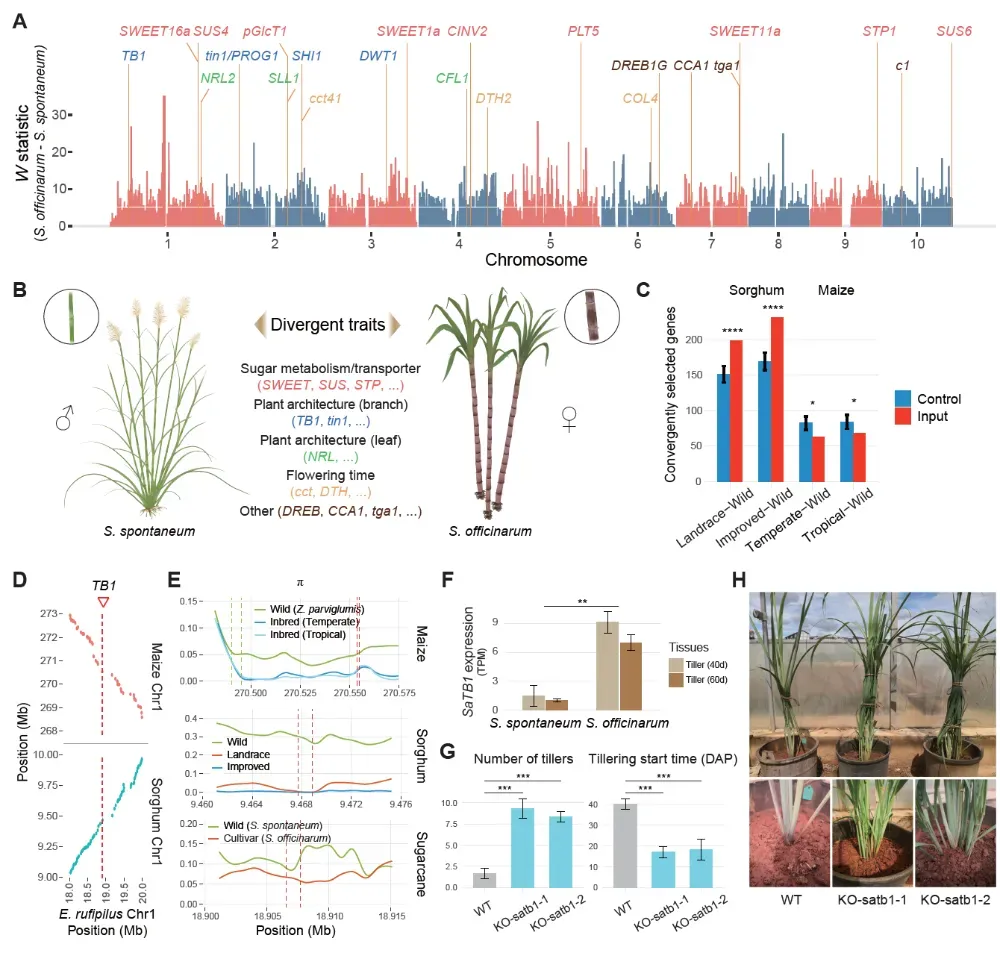
图5. 基于图泛基因组的甘蔗群体基因组学分析及其重要农艺性状趋同选择研究
六、新一代 GWAS:用“剂量”而不是“0/1/2”刻画多倍体针对多倍体
作物中传统基因组关联分析(GWAS)难以准确刻画等位剂量信息的难题,研究团队在图谱泛基因组框架下提出了剂量感知关联分析新方法(DosageGWAS)。该方法依托超级泛基因组和图结构比对,对等位位点进行连续剂量估算,并在统计模型中综合考虑不同同源及同源异源染色体上的等位剂量,从而突破了二倍体“0/1/2”模型在混倍体作物中的应用限制。与基于线性参考的常规 GWAS 相比,“图谱 + DosageGWAS”框架显著提高了关联分析的灵敏度和解释力,不仅检测到更多显著关联位点,而且对糖分性状和叶片角度性状的遗传力解释度由约 0.56/0.58 提升至 0.62/0.78,独立验证的剂量差异位点数量也明显增加。在该框架下,研究成功鉴定出两个具有代表性的关键候选基因。其一是 SaIRX10,位于甘蔗第 9 号染色体约 57 Mb 区域,在 8 项糖分相关性状中有 6 项表现出显著关联。该基因为水稻细胞壁合成基因 IRX10 的同源基因,在甘蔗中,其与高糖相关的衍生等位剂量在驯化过程中呈持续累积和固定趋势,显示出明显的正向选择信号。其二是 SaBAK5,作为叶片角度和株型调控的关键因子,在第 3 号染色体启动子区域集中富集多个显著关联位点;等位剂量越高,其表达水平越低,对应叶片越直立,相关有利等位在现代栽培甘蔗中显著富集,说明株型改良已成为近现代育种的重要方向之一。上述结果证明,在混倍体作物中精确量化“等位剂量”并纳入统计模型,是打破“隐匿遗传力”和提升关联分析信号的关键。
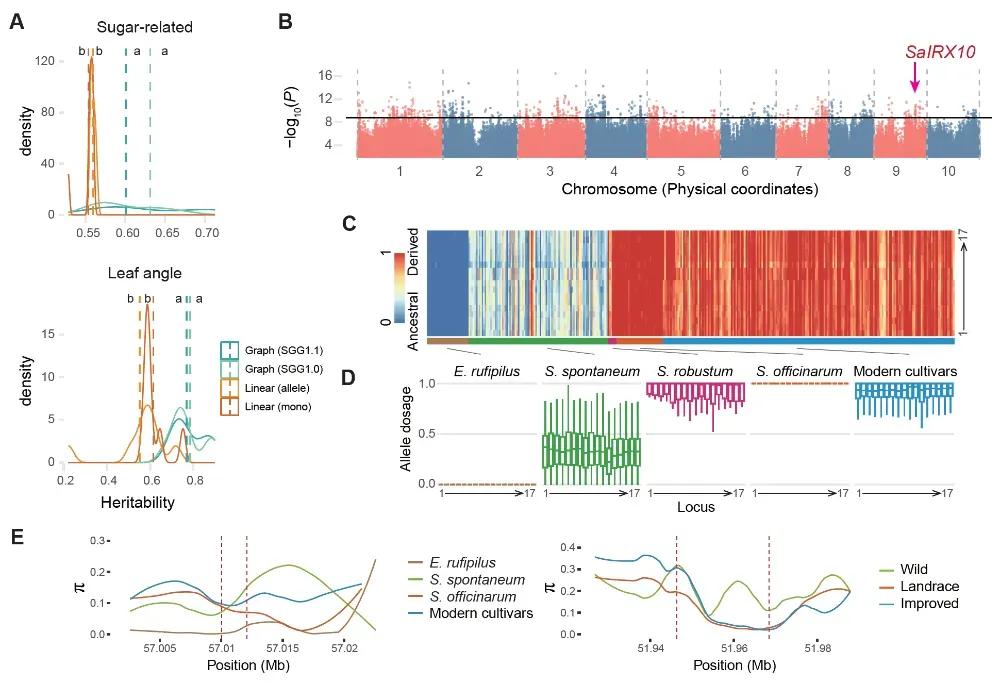
图6. 基于图泛基因组的剂量GWAS分析与关键位点挖掘
七、不仅是甘蔗:向小麦、棉花、马铃薯等多倍体作物推广
为验证方法的普适性,研究团队将这一多尺度图谱泛基因组策略推广至异源多倍体小麦、棉花以及同源多倍体马铃薯等多倍体物种。通过对这三类典型多倍体作物构建图谱超级泛基因组并进行比对,结果显示,构建的图谱超级泛基因组能够捕获约 94–97% 的基因组多样性,远高于最佳单一参考基因组的 48–65%,同时显著提升了读段比对质量,弥补了因结构变异而丢失的多样性信息。在马铃薯小规模 GWAS 实验中,该方法同样提升了关联信号和遗传力解释度。这表明,“多尺度图谱 + 剂量感知 GWAS”框架不仅适用于甘蔗,也可跨物种、跨多倍体作物广泛推广,为复杂作物基因组研究和分子育种提供通用工具。
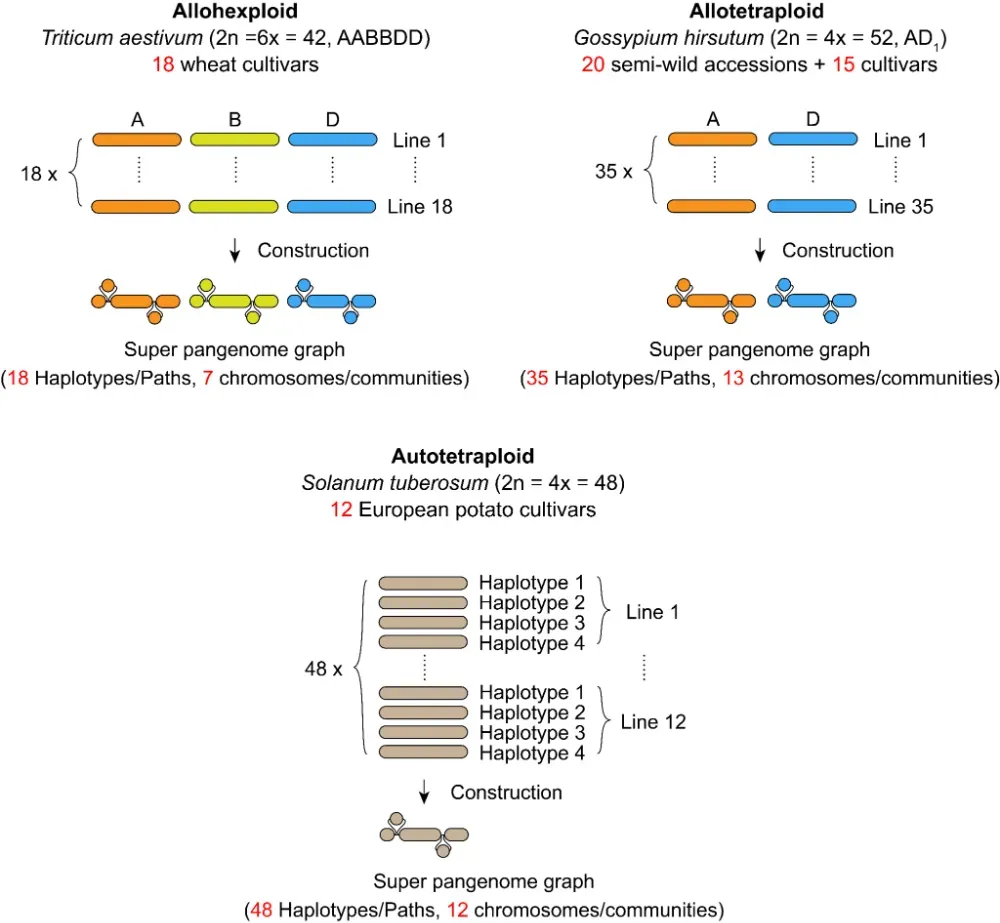
图7. 多尺度图泛基因组策略同样适用于异源多倍体(小麦、棉花)与同源多倍体(马铃薯)
八、意义与展望:为复杂作物“换代”的基础设施
长期以来,现代甘蔗育种高度依赖有限的亲本材料,遗传基础狭窄、种质资源利用不足,制约了产量和抗逆性进一步提升。本研究构建的甘蔗多尺度图谱泛基因组及配套分析流程,有望在多个层面加速育种进程。一是支撑高质量分子标记开发与基因组预测。该体系提供了剂量精确、结构信息丰富的大规模变异数据,可设计适用于多倍体的单剂量标记和高密度芯片,并将剂量感知信息纳入基因组预测模型,有望显著提高多倍体作物的选择准确度,加快早代材料淘汰和优系筛选。二是高效挖掘野生与稀有优良等位。依托图谱开展跨物种比较和群体扫描,可快速锁定来源于野生近缘种或地方品种的抗病、抗逆、高糖、高纤维等优良等位,为“回交导入+基因编辑”提供精准靶点。三是为未来“甘蔗泛基因组联盟”奠定基础。随着中国种、印度种等历史品种和区域性地方品种基因组的不断发布,现有甘蔗属超级泛基因组可持续扩展,逐步形成覆盖全球甘蔗种质的动态演进型“甘蔗基因资源基础设施”。
研究团队同时指出,图谱泛基因组仍面临转录组标准化分析工具不足、复杂重复区域的计算效率,以及不同同源或同源异源拷贝间拷贝数与表达定量缺乏统一标准等挑战。随着相关算法、比对软件和下游分析工具的持续发展,图谱泛基因组有望逐步取代单一线性参考,成为复杂作物基因组学与分子育种的新型基础设施。
该研究以广西大学为第一通讯单位和共同第一作者单位,标志着我国在甘蔗图泛基因组与多倍体遗传解析领域取得重大突破。研究成果系统突破了多倍体遗传解析的关键技术瓶颈,精准定位了分蘖、糖分等一批重要农艺性状相关基因及其调控元件,并已直接服务于甘蔗高糖、高产分子育种实践。在百余份材料中完成糖分性状关联分析,在遗传多样性捕获、关键性状定位和育种靶标挖掘等方面取得显著成效,为多倍体作物分子设计育种提供了核心技术支撑,应用前景广阔。
该论文的共同第一作者均为张积森教授团队成员,分别为福建农林大学黄育敏博士、广西大学研究助理张以星(唐海宝教授与张积森教授联合培养研究生,现张积森教授团队科研助理)和广西大学张清教授。广西大学张积森教授为第一通讯作者,福建农林大学唐海宝教授为共同通讯作者。参与本研究的广西大学张积森教授团队成员还包括庄桂(博士研究生)、汪柏宇(博士研究生)、高瑞婷(博士研究生)、石会红(博士后)、徐益副教授、华秀婷副教授、徐秋涛教授等。此外,广西大学姚伟教授、陈保善教授和张木清教授也参与了本研究。来自福建农林大学的齐浥颖(现山东农业大学副教授,张积森教授团队已毕业博士生)、明瑞光教授,云南甘蔗研究所李纯佳副研究员、刘新龙研究员,以及仲恺农业工程学院齐永文教授等也为研究提供了重要支持。本研究得到国家重点研发计划、国家自然科学基金、广西科技重大专项、广西重点研发计划等多个项目的联合资助。
论文链接:
https://www.science.org/doi/10.1126/science.adx1616
专家点评
从甘蔗到复杂多倍体作物:图泛基因组引领复杂基因组育种新时代
韩斌(中国科学院院士)
张积森团队长期致力于甘蔗基因组与分子育种研究,以基因组学为主要手段,从关键基因挖掘到功能验证,系统攻克了多倍体基因组研究中的核心难题。在前期完成野生种与现代栽培甘蔗高质量基因组构建、解析染色体数目演化规律和基因剂量效应的基础上,张积森团队在发表于《Science》的研究工作中(Huang et al., 2026),构建了首个面向混合倍性甘蔗种质的多尺度图泛基因组,统一整合了多个物种和数十条单倍型信息,实现了在同一坐标系下对结构变异、拷贝数差异及剂量敏感位点的精确表征。
依托这一框架,团队发展了适用于多倍体的剂量型关联分析方法(DosageGWAS),系统挖掘出调控碳同化、糖分积累和细胞壁性状等关键农艺性状的剂量依赖基因,并通过代表性基因(如 SaTB1)的功能验证,将图泛基因组层面的发现直接链接到产量等表型改良。该研究不仅彻底改写了人们对甘蔗基因组“不可解”的传统认知,还为将甘蔗这一高复杂度基因组作物推进至可设计育种提供了一条通用技术路线,为小麦、苜蓿、马铃薯等复杂多倍体作物的精准改良提供了重要范式。
突破多倍体基因组解析极限,引领甘蔗育种新范式。
刘耀光(中国科学院院士)
甘蔗作为全球重要的糖料和能源作物,其基因组兼具同源、异源与非整倍体特征,结构极为复杂,被视为植物基因组学中最难解析的作物之一。长期以来,缺乏高质量甘蔗参考基因组和匹配的遗传分析框架,严重制约了甘蔗性状解析与分子育种进展。
在前期解析甘蔗品种割手密基因组及种质资源演化的基础上(Nature Genetics, 2018, 2022),广西大学亚热带农业生物资源保护与利用国家重点实验室张积森团队近年来在甘蔗基因组研究方面取得系列突破,先后构建了现代栽培甘蔗超复杂参考基因组及种质资源演化图谱(Nature Genetics, 2025),解析了甘蔗近缘种蔗茅的无缺口高质量基因组并阐明甘蔗属多倍体起源(Nature Plants, 2023),为甘蔗分子遗传研究奠定了坚实基础。然而,传统线性参考在解析甘蔗多倍体、高杂合、高重复基因组时仍存在明显局限,难以充分捕捉其丰富的结构变异与等位基因多样性。
此次发表于《Science》的研究“Multiscale pangenome graphs empower the genomic dissection of mixed-ploidy sugarcane species”(《多尺度泛基因组图谱赋能混合倍性甘蔗的基因组解析》),标志着甘蔗基因组学与遗传学研究迈入新阶段。该工作构建了多尺度图泛基因组框架,在统一坐标空间紧凑表征复杂多倍体单倍型及等位基因剂量,整合4个甘蔗物种9套基因组,捕获约82%的遗传多样性,显著优于单一参考约34%的覆盖水平。此研究原创提出的 DosageGWAS 方法强化了变异发现与性状解释能力,有效破解了植物多倍体“难分型、难比对、难关联”的核心瓶颈,精准定位了甘蔗分蘖、糖分等关键农艺性状相关基因及调控元件,直接支撑了甘蔗百余份种质的性状关联分析和标记设计,显著提升了基因组选择和性状预测的准确性。
值得强调的是,本研究提出的图超泛基因组构建通用策略同样适用于其它植物同源多倍体(如小麦、棉花)和自交多倍体(如马铃薯),可在统一框架下区别处理不同倍性类型,为混合倍性作物组学研究和分子育种提供可复制的技术蓝本与系统性方法范式。
我国是甘蔗种植与蔗糖生产大国,保障糖业安全关乎国计民生。该成果不仅在甘蔗基础研究领域巩固和提升了我国的国际引领地位,也为其他多倍体作物的分子育种提供了系统技术支撑,彰显了从基础前沿突破到产业关键问题解决的贯通式创新,对推动我国甘蔗种业振兴与糖业高质量发展具有重要示范意义。
甘蔗异源多倍体遗传解析与分子育种的新范式
张献龙(中国工程院院士)
多倍体在自然界普遍存在,超半数的植物是多倍体,多倍体的显著优势主要体现在两个方面,一是生物量大,可以为人类生产更多的食物;而是综合抗逆性强、适应性广,可以利用贫瘠的土壤。甘蔗是目前已知最复杂的异源多倍体系之一:高度杂合、染色体数目不整齐,等位基因剂量多层次叠加,单剂量位点与多剂量位点组合在基因组中错综分布,使基于单一参考基因组和二倍体假设的传统遗传解析与分子设计难以奏效。基于在甘蔗多倍体基因组学与遗传学领域的长期积累,张积森团队在近期发表于《Science》的研究(Huang et al., 2026)中构建了面向混合倍性甘蔗种质的多尺度图泛基因组,将不同物种来源、不同拷贝数及剂量状态的单倍型统一映射到同一坐标系,为异源多倍体“还原”出一个可计算、可推理的遗传框架。
依托这一框架发展出的剂量敏感变异识别方法与dosageGWAS,解决了目前甘蔗中不能精确定位与碳同化、糖分积累和细胞壁性状等关键农艺性状相关等位变异的难题,使单剂量与多剂量状态下的效应差异解析成为可能,从而为异源多倍体中特有的剂量效应及互作模式分析提供了范式。通过将代表基因功能验证与图泛基因组解析紧密衔接,该研究为甘蔗这一“非整体”的复杂多倍体基因组建立了可操作的遗传—育种路径,突破了复杂多倍体领域长期悬而未解的关键难题,也为复杂多倍体作物在真实剂量背景下开展精细遗传改良提供了可推广、可操作的技术路线。
参考文献:Yumin Huang#, Yixing Zhang#, Qing Zhang#, Gui Zhuang, Chunjia Li, Baiyu Wang, Ruiting Gao, Yi Xu, Yiying Qi, Xiuting Hua, Huihong Shi, Qiutao Xu, Wei Yao, Xinlong Liu, Yongwen Qi, Baoshan Chen, Muqing Zhang, Ray Ming, Haibao Tang*, Jisen Zhang*. Multiscale pangenome graphs empower the genomic dissection of mixed-ploidy sugarcane species. Science 391, eadx1616 (2026).Jisen Zhang*#, Yiying Qi#, Xiuting Hua#, Yongjun Wang#, Baiyu Wang#, Yongwen Qi#, Yumin Huang#, Zehuai Yu#, Ruiting Gao#, Yixing Zhang , Tianyou Wang, Yuhao Wang , Jing Mei , Qing Zhang , Gang Wang , Haoran Pan, Zhen Li, Shuangyu Li , Jia Liu , Nameng Qi , Xiaoxi Feng, Mingxing Wu , Shuqi Chen , Cuicui Du , Yihan Li , Yi Xu , Yaxue Fang , Panpan Ma , Qingyun Li , Yuanchang Sun , Xiaomin Feng , Wei Yao , Muqing Zhang , Baoshan Chen, Xinlong Liu , Ray Ming , Jianping Wang , Zuhu Deng , Haibao Tang. The highly allo-autopolyploid modern sugarcane genome and very recent allopolyploidization in Saccharum. Nature Genetics 57, 242-253 (2025).Tianyou Wang#, Baiyu Wang#, Xiuting Hua#, Haibao Tang#, Zeyu Zhang, Ruiting Gao, Yiying Qi, Qing Zhang, Gang Wang, Zehuai Yu, Yongji Huang, Zhe Zhang, Jing Mei, YuhaoWang, Yixing Zhang, Yihan Li, Xue Meng, Yongjun Wang, Haoran Pan, Shuqi Chen, Zhen Li, Huihong Shi, Xinlong Liu, Zuhu Deng, Baoshan Chen, Muqing Zhang, Lianfeng Gu, Jianping Wang, Ray Ming, Wei Yao*, Jisen Zhang*. A complete gap-free diploid genome in Saccharum complex and the genomic footprints of evolution in the highly polyploid Saccharum genus. Nature Plants 9, 554-571 (2023).Qing Zhang#, Yiying Qi#, Haoran Pan#, Haibao Tang#, Gang Wang, Xiuting Hua, Yongjun Wang, Lianyu Lin, Zhen Li, Yihan Li, Fan Yu, Zehuai Yu, Yongji Huang, Tianyou Wang, Panpan Ma, Meijie Dou, Zongyi Sun, Yibin Wang, Hengbo Wang, Xingtan Zhang, Wei Yao, Yuntong Wang, Xinlong Liu, Maojun Wang, Jianping Wang, Zuhu Deng, Jingsheng Xu, Qinghui Yang, ZhongJian Liu, Baoshan Chen, Muqing Zhang, Ray Ming, Jisen Zhang*. Genomic insights into the recent chromosome reduction of complex autopolyploid sugarcane S. spontaneum. Nature Genetics 54, 885-896 (2022).Jisen Zhang*#, Xingtan Zhang#, Haibao Tang#, Qing Zhang#, Xiuting Hua, Xiaokai Ma, ..., Chifumi Nagai*,Ray Ming*. Allele-defined genome of the autopolyploid sugarcane Saccharum spontaneum L.. Nature Genetics 50, 1565-1573 (2018).
转载自 | BioArt植物